Resumos
Os produtos de origem avícola podem ser importantes veículos de transmissão de Salmonella spp. para humanos e, dentre os vários parâmetros que determinam a qualidade de um alimento, destacam-se os que definem suas características microbiológicas. Objetivou-se detectar e quantificar Salmonella spp. na tecnologia de abate de frangos de corte por microbiologia convencional (MC) e número mais provável miniaturizado (mNMP). As coletas foram realizadas em duas visitas a três abatedouros sob Inspeção Federal e em seis pontos de coleta em triplicata, definidos como: recepção das aves (swabs de cloaca e esponjas de gaiolas de transporte antes e após a higienização) e carcaças (após pré resfriamento em chiller, após o gotejamento e antes da embalagem primária e congeladas a -12oC por 24 horas), totalizando 108 amostras. Identificou-se Salmonella spp. em três dos seis pontos do fluxograma de abate e em dois dos três estabelecimentos amostrados, independentemente do método utilizado, perfazendo 5,5% de positividade, onde destaca-se a contaminação nas gaiolas de transporte das aves após a higienização. Não foi possível correlacionar os resultados da microbiologia convencional e do mNMP ou mesmo quantificar a contaminação ao longo da tecnologia de abate, o que indica a necessidade de se utilizar um método qualitativo aliado ao método de quantificação quando Salmonella estiver presente em quantidades inferiores ao limite de detecção do mNMP proposto (0,13 NMP/mL). Os sorovares identificados foram Typhimurium, Panama, Lexington e Rissen, consideradas paratíficos e, portanto, potencialmente capazes de causar infecções em humanos, embora estes sorovares não tenham sido isolados em produtos finais e sim na chegada dos frangos aos abatedouros (swabs de cloaca e gaiolas de transporte). A identificação de Salmonella spp. nas gaiolas de transporte após a higienização é um indicativo da necessidade de revisão e adequação dos métodos automatizados de lavagem atualmente utilizados nos abatedouros.
Salmonella spp.; número mais provável miniaturizado; sorovares; frangos de corte.
Poultry products can be important modes of transmission of Salmonella spp. to humans and, among several parameters used to determine food quality, microbiological characteristics play an essential role. The aim of this study was to determine and quantify Salmonella spp. at broiler slaughtering facilities. This was done by conventional microbiology and by the miniaturized most probable number (mMPN) methods. Three federally-inspected slaughterhouses were visited, where samples were collected in triplicate from six sites: reception of live birds (cloacal swabs and sponge samples from transport cages before and after sanitation) and carcass processing (after pre-chiller, after dripping, and before primary packaging and refrigeration at -12oC for 24h), totaling 108 samples. Three of the six surveyed sites and two of the three slaughterhouses were contaminated with Salmonella spp., showing an infection rate of 5.5% independently of the method used, and revealing that transport cages were contaminated after sanitation. No correlation could be established between the results of conventional microbiology and mMPN methods, and contamination along the slaughtering line could not quantified. This indicates the importance of combining qualitative and quantitative methods for the enumeration of Salmonella when detection rates are lower than the proposed mMPN limit (0.13 MPN/mL). Typhimurium, Panama, Lexington and Rissen, which are paratyphoid organisms and are potentially infectious to humans, were identified. However, these serovars were isolated at the reception of live birds (from cloacal swabs and from transport cages) rather than from the end products. Given that Salmonella spp. was detected in transport cages after sanitation, it is paramount that automated washing procedures currently used in slaughterhouses be reassessed and adjusted.
Salmonella spp.; miniaturized most probable number; serovars; poultry slaughterhouses.
Introdução
Infecções por Salmonella são associadas à criação intensiva das aves e à surtos de salmonelose clínica, visto que as contaminações podem ocorrer tanto por contato entre aves sadias e infectadas como por contaminação cruzada nos abatedouros, onde o número de bactérias é variável nas diferentes etapas da tecnologia de abate. Análises microbiológicas desde o campo até os produtos finais são fundamentais para estimar a extensão da carga microbiana e avaliar os efeitos dos métodos de controle sanitário utilizados nos frigoríficos, como as Boas Práticas de Fabricação (BPF), Procedimento Padrão de Higiene Operacional (PPHO) e Análise de Perigos e Pontos Crítico de Controle (APPCC).
A pesquisa de Salmonella spp. para avalição da contaminação em abatedouros por métodos qualitativos já é realizada, mas a quantificação da bactéria não é rotineiramente empregada, uma vez que técnicas tradicionais de enumeração como o Número Mais Provável (NMP), que utilizam séries de tubos múltiplos, demandam tempo, pessoal e recursos financeiros elevados (Cavada et al. 2010Cavada C.A., Cardoso F.M. & Schimidt V. 2010. Comparison of three me-thods for Salmonella sp. quantification in wastwater. Acta Scientiae Veterinariae 38(1):17-23.), dificultando sua aplicação em programas de monitoria. Métodos de quantificação de bactérias por Número Mais Provável miniaturizado (mNMP) são citados como uma alternativa mais rápida e menos trabalhosa para enumeração de salmonelas (Fravallo et al. 2003Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88., Pavic et al. 2009Pavic A., Groves P.J., Bailey G. & Cox J.M. 2009. A validated miniaturized MPN method, based on ISO 6579:2002, for the enumeration of Salmonella from poultry matrices. J. Appl. Microbiol. 109:25-34.) mas foram aplicados em amostras artificialmente contaminadas para validação destas técnicas.
Infecções por Salmonella spp. são classificadas em enfermidades típicas de aves, causadas pelos sorovares Pullorum e Gallinarum, e enfermidades paratíficas, originadas por mais de 2500 sorovares não específicos potencialmente capazes de produzir infecções alimentares em humanos. Destes, cerca de 10% são isolados em aves, uma vez que a distribuição de salmonelas oriundas de fontes avícolas é geograficamente variável e alterna-se com o passar dos anos (Gast et al. 2007Gast R., Guraya R. & Guard-Bouldin J. 2007. Colonization of specific regions of the reproductive tract and deposition at different locations inside eggs laid by hens infected with Salmonella Enteritidis or Salmonella Heidelberg. Avian Dis. 51:40-44.).
Assim, devido à importância do controle de Salmonella spp. na produção avícola e o risco potencial em saúde pública, objetivou-se utilizar o método microbiológico convencional e Número Mais Provável miniaturizado (mNMP) para identificação e quantificação de Salmonella spp. em diferentes pontos da tecnologia de abate de frangos de corte bem como relatar os sorovares isolados nos pontos positivos para a bactéria.
Material e Métodos
Amostragem e pontos de coleta nos abatedouros
As coletas foram realizadas em três abatedouros de frangos de corte (A, B e C) sob Serviço de Inspeção Federal (SIF) no sul do Brasil, entre setembro de 2013 e janeiro de 2014, com duas visitas em cada abatedouro. Determinou-se seis pontos de coleta em função dos resultados de estudos anteriores (dados não mostrados) que apontaram estes pontos com positividade para Salmonella spp., como segue: recepção das aves (swabs de cloaca e esponjas de gaiolas de transporte antes e após a higienização) e carcaças após pré resfriamento em chiller, após o gotejamento e imediatamente antes da embalagem primária e carcaças congeladas a -12oC por 24 horas.
Cada um dos pontos foi coletado em triplicata, totalizando 108 amostras, que foram processadas no Laboratório de Bacteriologia do Hospital Veterinário da (UPF) por microbiologia convencional (MC) e número mais provável miniaturizado (nNMP), perfazendo 240 ensaios para detecção e quantificação de Salmonella spp, respectivamente, incluindo os controles negativo (E. coli ATCC 25992) e positivo (Salmonella Enteritidis ATCC 13076). Todo o material coletado foi transportado sob refrigeração e imediatamente processado quando da chegada ao laboratório. O método de microbiologia convencional para isolamento de Salmonella spp. seguiu a ISO 6579 (2002) e o método de mNMP utilizado foi descrito por Fravallo et al. (2003)Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88. e adaptado por Colla et al. (2014)Colla F.L., Mion L., Parizotto L., Rodrigues L.B., Pilotto F., Dickel E.L., Nascimento V.P. & Santos L.R. 2014. Miniaturized most probable number for the enumeration of Salmonella sp in artificially contaminated chicken meat. Revta Bras. Ciênc. Avícola 16(1):45-48..
Processamento das amostras Swabs de cloaca
Para os swabs cloacais foram amostradas 300 aves em cada coleta, sendo utilizado um swab para cada duas aves, compondo um pool de 50 swabs que foram acondicionados em frascos com 50 mL de água peptonada tamponada (APT 1,0%). No laboratório, homogeneizou-se os pools e retirou-se alíquotas de 17,5 mL, sendo 7,5 mL destinados ao mNMP e 10 mL à microbiologia convencional.
Esponjas de gaiolas de transporte
As gaiolas de transporte foram identificadas com lacres oficiais para controle de retirada das mesmas após a higienização no sistema automatizado de lavagem utilizado nos abatedouros avaliados. A amostragem foi realizada com esponjas bacteriológicas com neutralizante (Sponge Stick Neutraling Buffer 3M) por toda a extensão interna da gaiola, antes e após a lavagem e sanitização. As esponjas foram acondicionadas em saquetas fornecidas pelo fabricante e no laboratório adicionados 50mL de APT 1,0%. Homogeneizou-se as amostras e retirou-se 17,5mL para as demais análises (7,5mL para mNMP e 10mL para MC).
Carcaças
As carcaças foram acondicionadas em sacos plásticos individuais e identificadas com lacres oficiais. No laboratório adicionou-se 400 mL de APT 1,0% para rinsagem das carcaças e retirou-se 17,5 mL para as análises subsequentes.
Pesquisa de Salmonella spp. por microbiologia convencional
Alíquotas de 10mL de APT 1,0% foram incubadas a 37±1°C por 16 a 20 horas e repicadas em meios seletivos, sendo 1mL em 9mL de caldo Tetrationato (incubação a 37±1°C por 24±3 horas) e 100μL em 9,9mL de caldo Rappaport-Vassiliadis (incubação a 41,5±1°C por 24±3 horas). O plaqueamento das amostras foi realizado em Agar Rambach (Merck®) e Agar Verde Brilhante Novobiocina (BGN - Brilhant Green Novobiocina) por esgotamento com alça de platina e as placas incubadas a 37±1°C por 24±3 horas. Colônias sugestivas de Salmonella spp. foram submetidas as provas de TSI (Triple Sugar Iron), LIA (Lysine Iron Agar), SIM (Sulfite- Indole-Motility), caldo ureia e sorologia com soro polivalente anti-O. A identificação final dos isolados foi realizada por microarray (Chek & Trace® Salmonella).
Quantificação de Salmonella spp. por Número Mais Provável miniaturizado (mNMP)
Para quantificação de Salmonella spp. nas amostras naturalmente contaminadas foi utilizado o método do mNMP proposto por Fravalo et al. (2003)Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88. e adaptado por Colla et al. (2014)Colla F.L., Mion L., Parizotto L., Rodrigues L.B., Pilotto F., Dickel E.L., Nascimento V.P. & Santos L.R. 2014. Miniaturized most probable number for the enumeration of Salmonella sp in artificially contaminated chicken meat. Revta Bras. Ciênc. Avícola 16(1):45-48., que contém as mesmas fases da microbiologia convencional mas executadas em placas de 24 poços com capacidade para 2,5mL. Previamente ao experimento foram realizados ensaios para determinar o limite de detecção do mNMP em amostras de carne de frango artificialmente contaminadas com Salmonella Enteritidis ATCC 13076, que apontaram um limite de 0,13 NMP/mL. Na condução do experimento utilizou-se os 7,5mL oriundos do processamento das amostras e transferiu-se 2,5mL para cada um dos poços das três primeiras cavidades na primeira linha das placas, representando uma amostra. Destes, 0,5 mL de cada cavidade foram transferidos para 2 mL de água peptonada 1,0%, previamente vertidos nas linhas seguintes na mesma placa. Três diluições sucessivas foram realizadas da mesma maneira. As placas foram então incubadas para o pré-enriquecimento a 37±1°C por 16 a 20 horas.
Para enriquecimento seletivo utilizou-se Rappaport-Vassiliadis Semisolid Modified (MSRV) com novobiocina. O MSRV é uma modificação do caldo de enriquecimento Rapapport Vassiliadis, tornando-o semi-sólido, o que permite a detecção visual de motilidade bacteriana pela formação de um halo em torno do ponto de inoculação (Baggensen et al. 2001Baggensen D.L., Bagger J., Mogelmose V., Nielsen B., Svensmark B. & Olsen J.E. 2001. Quantification of DT104 in slurry from infected pigs. Report on the 6th CRL-Salmonella Workshop, Bilthoven, Netherlands, p.30-32.).
Após o pré-enriquecimento, as placas foram mantidas em agitação orbital por três a cinco minutos e, com pipetador multicanal, transferiu-se 20μL de cada poço para a cavidade correspondente em outra placa contendo 2mL de MSRV, incubando-as por 24 a 48 horas a 41,5±0,5°C. Após este período, a viragem da cor azul esverdeada do meio MSRV para a cor branca ou azul claro era indicativa de crescimento bacteriano, o que era confirmado pela semeadura do conteúdo destes poços em Agar Rambach®. Colônias com crescimento compatível com Salmonella spp. foram semeadas em Agar não seletivo, incubadas a 37±1°C por 18 a 24 horas e submetidas a confirmação bioquímica e sorológica como na microbiologia convencional.
Cálculo do Número Mais Provável miniaturizado
Caracterizou-se como positivos os poços que tiveram isolamento de Salmonella spp. confirmado pelos testes bioquímicos e soro polivalente anti-O. A partir destes resultados foram estabelecidos os poços positivos e negativos usados para o cálculo do número mais provável (NMP) de diluições seriadas não decimais utilizando uma fórmula simplificada (Thomas, 1942Thomas H.A. 1942. Bacterial densities from fermentation tube tests. J. Am. Water Assoc. 34:572-576.), como segue:
NMP / g ou mL = P / √NT
Sendo:
P = número de tubos positivos;
N = soma da quantidade de amostra inoculada em todos os tubos negativos;
T = soma da quantidade de amostra inoculada em todos os tubos.
No método utilizado inoculou-se 2,5 mL em três poços na linha A das placas (A1, A2, A3), determinando-se a primeira linha (A) de poços como amostra inicial (1:1), e a segunda (B) como 1:5. Seguiu-se a diluição seriada não decimal na base 5, obtendo-se, deste modo, as diluições 1:1, 1:5, 1:25, 1:125, com volumes de alíquotas respectivamente de 2 mL, 0,5 mL, 0,1 mL e 0,02 mL. Aplicando-se a fórmula de Thomas (1942)Thomas H.A. 1942. Bacterial densities from fermentation tube tests. J. Am. Water Assoc. 34:572-576. para cálculo do resultado a partir da combinação de tubos 2:0:0:0 em séries de três tubos, utilizou-se os volumes das alíquotas para cálculo do NMP, como segue:
NMP / mL = P / √NT
Sendo: P = 2 + 0 + 0 +0 = 2
N = (1 x 2) + (3 x 0,5) + (3 x 0,1) + (3 x 0,02) = 2 + 1,5 + 0,3 + 0,06 = 3,86
T = (3 x 2) + (3 x 0,5) + (3 x 0,1) + (3 x 0,02) = 6 + 1,5 + 0,3 + 0,06 = 7,86
Portanto:
NMP / mL = 2 / √(3.86) x (7,86) = 2 / √30, 3396 = 2 / 5,51
NMP / mL = 0,36
A aplicação desta formula foi comparada com os resultados obtidos pelo programa MPN Calculator (Cariale, sem data), que possibilita o cálculo dos resultados padronizados pelo volume de amostra por teste, número de tubos e mais de 3 diluições. Calculou-se o NMP por mL e os limites mínimos e máximos do intervalo de confiança a 95% de probabilidade (IC 95%). Assim, utilizou-se o MPN Calculator para finalizar os cálculos das combinações de tubos obtidas neste trabalho, com combinação de tubos positivos em séries de 3, com quantidade inoculada de amostra de 2; 0,5; 0,1 e 0,02mL.
Para a obtenção do resultado final, referente à área das gaiolas, o NMP obtido pela combinação de poços positivos precisa ser convertido para NMP/cm2, utilizando o cálculo a seguir:
Resultados e Discussão
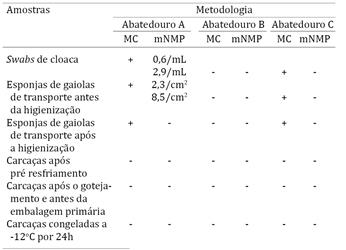
Identificou-se Salmonella spp. em três dos seis pontos do fluxograma de abate de frangos de corte e em dois dos três estabelecimentos amostrados, independentemente do método utilizado (Quadro 1), totalizando 5,5% de positividade (6/108).
A positividade para Salmonella spp. nos abatedouros amostrados (5,5%) foi inferior a citada por Santos et al. (2000)Santos D.M.S., Berchieri Jr A., Fernandes S.A., Tavechio A.T.& Amaral L.A. 2000. Salmonella em carcaças de frango congeladas. Pesq. Vet. Bras. 20(1):39-42. com 32%, ou Lillard (1990)Lillard H.S. 1990. The Impact of commercial processing procedures on the bacterial contamination and cross-contamination of broiler carcasses. J. Food Protection 53(3):202-204., que relatou 5% de positividade para Salmonella spp. na chegada das aves e uma contaminação de 36% após o processamento. Já Dickel et al. (2005)Dickel E.L., Santos L.R., Rodrigues L.B., Valle S.F. & Cecatti D. 2005. Ocorrência de Salmonella em abatedouros de aves com tecnologia totalmente automatizada (grande porte), semi automatizada (médio porte) e semi automatizada (pequeno porte). Higiene Alimentar, São Paulo, 19(131):62-67., Ribeiro et al. (2007)Ribeiro A.R., Kellermann A., Santos L.R. dos, Bessa M.C.& Nascimento V.P. do. 2007. Salmonella spp. in raw broiler parts: occurrance, antimicrobial resistance profile and phage typing of the Salmonella Enteritidis isolates. Braz. J. Microbiol. 38:296-299., Moreira et al. (2009)Moreira G.N., Rezende C.S.M., Carvalho R.N., Mesquita S.Q.P., Oliveira A.N. & Arruda M.L.T. 2009. Ocorrência de Salmonella sp. em carcaças de frangos abatidos e comercializados em municípios do estado de Goiás. Revta Inst. Adolfo Lutz 67(2):126-130., Duarte et al. (2009)Duarte D.A.M., Ribeiro A.R., Vasconcelos A.M.M., Santos S.B., Silva J.V.D., Andrade P.L.A. & Falcão L. 2009. Occurrence of Samonella spp. in broiler chicken carcasses and their susceptibility to antimicrobial agents. Braz. J. Microbiol. 40(3):569-573. e Simas et al. (2011)Simas V.S., Santos F.F., Gouvêa R., Aquino M.H.C., Abreu D.L.C., Nascimento E.R. & Pereira V.L.A. 2011.Pré-resfriamento na redução de coliformes em carcaças de frango de corte. Ciência Rural 43(9):1618-1622. referem variações de 3% a 39% no isolamento de Salmonella spp. em origens tão diversas quanto abatedouro e varejo.
Destaca-se que no presente trabalho o isolamento inicial da bactéria em swabs cloacais e gaiolas de transporte não foi confirmado nos produtos finais (carcaças resfriadas e congeladas), o que pode ser atribuído aos procedimentos de Boas Práticas de Fabricação, PPHO e APPCC adotados nos abatedouros amostrados. Quando pontos críticos da tecnologia de abate são adequadamente manejados, com renovação de água e temperaturas inferiores a 4ºC no chiller, por exemplo, ocorre redução da contaminação inicial por Salmonella spp. como citado por Dickel et al. (2005)Dickel E.L., Santos L.R., Rodrigues L.B., Valle S.F. & Cecatti D. 2005. Ocorrência de Salmonella em abatedouros de aves com tecnologia totalmente automatizada (grande porte), semi automatizada (médio porte) e semi automatizada (pequeno porte). Higiene Alimentar, São Paulo, 19(131):62-67. com redução de 70% para 20%, e Simas et al. (2011)Simas V.S., Santos F.F., Gouvêa R., Aquino M.H.C., Abreu D.L.C., Nascimento E.R. & Pereira V.L.A. 2011.Pré-resfriamento na redução de coliformes em carcaças de frango de corte. Ciência Rural 43(9):1618-1622., de 15,8% para 3,3% em carcaças de frango após o chiller. Estes efeitos são corrobados por Humphrey & Jorgensen (2006)Humphrey T. & Jorgensen F. 2006. Pathogens on meat and infection in animals. Establishing a relationship using Campylobacter and Salmonella as examples. Meat Science 74:89-97. ao citar que a contaminação inicial nas aves pode ser reduzida com higiene adequada na tecnologia de abate, ou ainda Patterson (1971)Patterson J.T. 1971. Microbiological aspects of poutry processing. Brit. Poult. Sci. 12:197-203., para quem a condição microbiológica da carcaça é influenciada pela planta de abate, qualidade da matéria prima, fluxograma e equipamentos, bem como eficácia da higienização.
Entretanto, mesmo com a adequação dos procedimentos adotados para redução de uma contaminação pré-existente por Salmonella spp. é premente que se revise o sistema automatizado de lavagem de gaiolas e a eficácia dos sanitizantes utilizados, uma vez que as gaiolas amostradas mantiveram a contaminação pela bactéria após higienizadas. A correta higienização dos caminhões e das gaiolas de transporte é fundamental porque são fontes potenciais de contaminação cruzada. Este relato é corrobado por Corry et al. (2002)Corry J.E.L., Allen V.M. & Hudson W.R. 2002. Sources of Salmonella on broiler carcasses during transportation and processing: modes of contamination and methods of control. J. Appl. Microbiol. 92:424-432., que ao analisar gaiolas de transporte quanto à presença de Salmonella spp. no descarregamento dos frangos e após a lavagem e desinfecção identificou os mesmos sorovares antes e após a higienização das gaiolas, geralmente refletindo os sorovares isolados a campo.
A técnica para pesquisa de Salmonella spp. em alimentos é um método clássico de presença/ausência, desenvolvido para garantir a detecção da bactéria em situações desfavoráveis como microbiota competidora, número reduzido de Salmonella e/ou células injuriadas por métodos de conservação como calor, congelamento e secagem. Dada a variedade de alimentos que podem conter Salmonella spp., estimar o número de células presentes em uma amostra tem sido um desafio. O número mais provável (NMP) para quantificação de Salmonella spp. é descrito por diversos autores em diferentes matrizes (Chen et al. 2013Chen L., Zhang J., Yang X., Wu Q. & Xu M. 2013. [Prevalence and characterization of Salmonella spp. from foods in South China]. [Article in Chinese] .Wei Sheng Wu Xue Bao 453(12):1326-1333., Mazengia et al. 2014Mazengia E., Samadpour M., Hill H.W., Greeson K., Tenney K., Liao G., Huang X. & Meschke J.S. 2014. Prevalence, concentrations, and antibiotic sensitivities of Salmonella serovars in poultry from retail establishments in Seattle, Washington. J. Food Protection 77(6):885-93., Ta et al. 2014Ta Y.T., Nguyen T.T., To P.B., Pham X., Le H.T., Thi G.N., Alali W.Q., Walls I. & Doyle M.P. 2014. Quantification, serovars, and antibiotic resistance of Salmonella isolated from retail raw chicken meat in Vietnam. J. Food Protection77(1):57-66., Wang et al. 2014Wang Y., Chen Q., Cui S., Xu X., Jianghui Zhu., Luo H., Wang D. & Li F. 2014. Enumeration and Characterization of Salmonella Isolates from Retail Chicken Carcasses in Beijing, China. Foodborne Pathogens and Disease 11(2):126-132., Yang et al. 2014Yang B., Cui Y., Shi C., Wang J., Xia X., Xi M., Wang X., Meng J., Alali W.Q., Walls I.& Doyle M.P. 2014. Counts, serotypes, and antimicrobial resistance of Salmonella isolates on retail raw poultry in the People's Republic of China. J. Food Protection 77(6):894-902.). Porém, os autores concluem que pesquisas adicionais são necessárias para ampliar a eficácia dos métodos de quantificação de patógenos em ambientes de produção comercial.
A avaliação e implantação de metodologias de NMP simplificadas, como o NMP miniaturizado, poderia ser uma alternativa para a quantificação rotineira de Salmonella spp. Entretanto, com o método utilizado neste trabalho, não foi possível correlacionar os resultados da microbiologia convencional e do mNMP ou mesmo quantificar a contaminação ao longo da tecnologia de abate de frangos de corte. A positividade para Salmonella spp. foi obtida pelos dois métodos apenas em duas amostras (swabs de cloaca e esponjas de gaiola de transporte antes da higienização, sendo 1,8% (2/108) pelo mNMP e 5,5% (6/108) pelo método microbiológico convencional (Quadro 1).
Estes resultados não confirmam os relatados por autores que mostraram diferentes formas de miniaturização do NMP para quantificação de Salmonella. Fravalo et al. (2003)Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88. propuseram uma metodologia de mNMP utilizando o MSRV para seleção de salmonelas móveis e posterior desenvolvimento em meios cromogênicos enquanto Pavic et al. (2009)Pavic A., Groves P.J., Bailey G. & Cox J.M. 2009. A validated miniaturized MPN method, based on ISO 6579:2002, for the enumeration of Salmonella from poultry matrices. J. Appl. Microbiol. 109:25-34. validaram uma metodologia de mNMP baseada na ISO 6579:2002 usando MRSV e demonstraram não haver diferença significativa entre o NMP tradicional e o miniaturizado. Os autores utilizaram o meio Rapapport Vassiliadis semi sólido (MRSV) para enriquecimento em dejetos de suínos e matrizes de origem avícola, respectivamente. Já Colla et al. (2014)Colla F.L., Mion L., Parizotto L., Rodrigues L.B., Pilotto F., Dickel E.L., Nascimento V.P. & Santos L.R. 2014. Miniaturized most probable number for the enumeration of Salmonella sp in artificially contaminated chicken meat. Revta Bras. Ciênc. Avícola 16(1):45-48. ao comparar os dois métodos, observaram que a técnica descrita por Fravalo et al. (2003)Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88. foi eficaz para quantificação de Salmonella spp. em matriz cárnea de origem avícola, enquanto que com a técnica descrita por Pavic et al. (2009)Pavic A., Groves P.J., Bailey G. & Cox J.M. 2009. A validated miniaturized MPN method, based on ISO 6579:2002, for the enumeration of Salmonella from poultry matrices. J. Appl. Microbiol. 109:25-34. não foi possível quantificar o patógeno, provavelmente relacionado com problemas na aquisição de insumos semelhantes aos utilizados na técnica original.
Os resultados do presente trabalho, que utilizou a metodologia de Fravalo et al (2003)Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88. adaptada por Colla et al. (2014)Colla F.L., Mion L., Parizotto L., Rodrigues L.B., Pilotto F., Dickel E.L., Nascimento V.P. & Santos L.R. 2014. Miniaturized most probable number for the enumeration of Salmonella sp in artificially contaminated chicken meat. Revta Bras. Ciênc. Avícola 16(1):45-48., podem ser inicialmente atribuídos a heterogeneidade das amostras, em concordância com Skjerve & Olsvik (1991)Skjerve E. & Olsvik O. 1991. Immunomagnetic separation of Salmonella from foods. Int. J. Food Microbiol. 14:11-18., ao citar que a matriz afeta a sensibilidade e a especificidade de um protocolo de isolamento e representaria ambientes críticos avícolas, que variam de amostras com baixa umidade e altamente úmidas (carcaças e água do tanque da escaldagem) até ambientes altamente competitivos (cecos e fezes) (USDA-FSIS 2008USDA-FSIS 2008. Compliance Guideline for Controlling Salmonella and Campylobacter in Poultry. 2nd ed. Food Safety Inspection Service, United States Department of Agriculture, Washington, DC. Available at <http://www.fsis.usda.gov> Accessed in March 2013.
http://www.fsis.usda.gov...
). Também o limite de detecção do mNMP (0,13 NMP/mL, dados não mostrados) ou os volumes diminutos utilizados no pré-enriquecimento e enriquecimento seletivo, em comparação com a microbiologia convencional, podem ter influenciado negativamente o isolamento e quantificação das amostras. Assim, é necessário utilizar um método qualitativo aliado ao método de quantificação, uma vez que quando Salmonella spp. estiver presente em quantidades inferiores ao limite de detecção do mNMP proposto a microbiologia convencional é mais eficiente para a detecção do patógeno.
Mesmo sem correlação entre os métodos para identificação e/ou quantificação de Salmonella spp. foi possível isolar os sorovares descritos no Quadro 2. Os sorovares identificados são paratíficos e, portanto, potencialmente capazes de causar infecções em humanos. Também, segundo o CODEX Alimentarius, a presença de qualquer sorovar de Salmonella spp. em um alimento é suficiente para classificá-los como impróprio para consumo, tanto no mercado nacional como no internacional. Mesmo que no presente trabalho Salmonella spp. não tenha sido isolada em produtos finais, a positividade nos abatedouros amostrados indica que as medidas de controle devem ser reforçadas visando a não contaminação dos produtos destinados ao consumo humano.
Sorovares de Salmonella isolados na tecnologia de abate de frangos de corte por microbiologia convencional (MC) ou mNMP 105.
Dentre os sorovares isolados, S. Typhimurium é frequentemente isolada em casos clínicos em suínos e humanos, além de apresentar multirresistência à antimicrobianos e capacidade de formar biofilmes como um fator determinante na contaminação de equipamentos na indústria (Castelijn et al. 2013Castelijn G.A.A., Parabirsing J.A., Zwietering M.H., Moezelaar R. & Abee T. 2013. Surface behavior of S. Typhimurium, S. Derby, S. Bradenburg and S. Infantis. Vet. Microbiol. 161: 305-314.). Em países como a Alemanha (Methner et al. 2011Methner U., Rammler N., Fehlhaber K. & Rösler U. 2011. Salmonella status of pigs at slaughter - Bacteriological and serological analysis. Int. J. Food Microbiol. 151:15-20.), Portugal (Gomes-Neves et al. 2012Gomes-Neves E., Antunes P., Tavares A., Themudo P., Cardoso M.F., Gärtner F., Costa J.M. & Peixe L. 2012. Salmonella cross contamination in swine abattoirs in Portugal: Carcasses, meat and meathandlers. Int. J. Food Microbiol. 157:82-87.), China (Yang et al. 2013Yang B., Qiao L., Zhang X., Cui Y., Xia X., Cui S., Wang X., Meng X., Ge W., Shi X., Wang D.& Meng J. 2013. Serotyping, antimicrobial susceptibility, pulse field gel electrophoresis analysis of Salmonella isolates from retail foods in Henan Province, China. Food Control, Guildford, 32:228-235.) e Inglaterra (Mueller-Doblies et al. 2013Mueller-Doblies D., Speed K. & Davies R.H. 2013. A retrospective analysis of Salmonella serovars isolated from pigs in Great Britain between 1994 and 2010. Prev. Vet. Med. 110:447-455.) é o sorovar mais isolado em carcaças de suínos, semelhante aos estudos em abatedouros no Brasil (Castagna et al. 2001Castagna S.M.F., Bessa M.C., Carvalho D.A., Cardoso M.& Costa M. 2001. Resistência a antimicrobianos de amostras de Salmonella sp. isoladas de suínos abatidos no estado do rio grande do sul. Arqs Fac. Vet. UFRGS. 29(1):44-49., Bessa 2006Bessa M.C. 2006. Caracterização fenotípica e genotípica de amostras de Salmonella entérica sorovar Typhimurium isoladas de suínos no Rio Grande do Sul. Tese de Doutorado em Ciências Veterinárias, Faculdade de Veterinária, Universidade Federal do Rio Grande do Sul, Porto Alegre. 144p., Borowsky et al. 2006Borowsky L.M., Bessa M.C., Cardoso M.& Avancini C.A.M. 2006. Sensibilidade e resistência de amostras de Salmonella Typhimurium isoladas de suínos abatidos no Rio Grande do Sul/Brasil frente aos desinfetantes químicos quaternário de amônio e iodofor. Ciência Rural 36(5):1474-1479., Müller et al. 2009Müller M., Schwarz P., Kich J.D.& Cardoso M. 2009. Perfil sorológico e de isolamento de Salmonella sp. em suínos no início da terminação e ao abate. Ciênc. Anim. Bras. 10(3):931-937., Kich et al. 2011Kich J.D., Coldebella A., Morés N., Nogueira M.G., Cardoso M., Fratamico P.M., Call J.E., Fedorka-Cray P. & Luchansky J.B. 2011. Prevalence, distribution, and molecular characterization of Salmonella recovered from swine finishing herds and a slaughter facility in Santa Catarina, Brazil. Int. J. Food Microbiol. 151:307-313.).
O sorovar Panama faz parte do sorogrupo D1 sendo regularmente isolado de alimentos, animais e água. É relacionado com gastroenterites em humanos e parece ser capaz de causar doenças mais invasivas do que outros sorovares, com relatos de bacteremia e meningite em crianças (Noel et al. 2010Noel H., Hofhuis A., De Jong R., Heuvelink A.E., De Jong R.& Jager C. 2010. Consumption of Fresh Fruit Juice: How a Healthy Food Practice Caused a National Outbreak of Salmonella Panama Gastroenteritis. Foodborne Pathogens and Disease 7(4):375-381.).
S. Rissen é pouco frequente em infecções em humanos e não tem um reservatório específico identificado, mas a importância deste sorovar está aumentando em países como a Tailândia, com ocorrência em água e alimentos, principalmente frutos do mar (Skovgaard 2005Skovgaard N. 2005. Current topics in food microbiology. Int. J. Food Microbiol. 99:107-111.). Na Finlândia, S. Rissen tem sido frequentemente isolada em aves desde 2003 (Bangtrakulnonth et al. 2004Bangtrakulnonth A., Pornreongwong S., Pulsrikarn C., Sawanpanyalert P., Hendriksen R.S., Wong D.M.A.L.F. & Aarestrup F.M. 2004. Salmonella serovars from humans and other sources in Thailand, 1993-2002. Emerg. Infect. Dis. 10:131-6.) e, no Brasil, há relatos de isolamento em humanos entre 1950 e 1990 (Kumar et al. 2001Kumar S., Sadana J.R. & Mishra S.K. 2001. Studies on clinical signs, growth response and haematological changes in Japanese quail (Coturnix coturnix japonica) infected with Salmonella typhimurium. Indian J. Poult. Sci. 36:335-337.). No entanto, o risco para a população brasileira estaria relacionado principalmente ao consumo de carne suína, uma vez que o sorovar é comumente isolado nesta espécie (Fernandes et al. 2006Fernandes S.A., Tavechio A.T., Ghilardi A.C.R., Dias A.M.G., Almeida I.A. & Melo L.C.V. 2006. Salmonella serovars isolated from humans in São Paulo State, Brazil, 1996-2003. Revta Inst. Med. Trop. São Paulo 48: 174-189.).
Segundo Hofer et al. (2007)Hofer E., Silva S.J. & Reis E.M.F. 2007. Prevalência de sorovares de Salmonella isolados de aves no Brasil. Pesq. Vet. Bras. 18(1):21-27. a S. Lexington não é rotineiramente isolada em aves comerciais no Brasil, mas já foi relatada em carne de pato comercializada no varejo no Vietnã (Phan et al. 2005Phan T.T., Khai L.T., Ogasawara N., Tam N.T., Okatani A.T., Akiba M. & Hayashidani H. 2005. Contamination of Salmonella in retail meats and shrimps in the Mekong Delta, Vietnam J. Food Protection 68:1077-1080., Benajssaum et al. 2007Benajssaum B.R., Gallasum N., Troudium B.H., Belhadjum B. & Belhadium A.B. 2007. Trends in Salmonella entérica serotypes isolated from food, humans, animals and environment in Tunisia, 1994-2004. J. Infection 55:324-339.). Berchieri et al. (2013)Berchieri J., Freitas Neto O.C., Angela H.L., Soares N.M., Guastalli E.A.L. & Almeida A.M. 2013. Salmonella spp. in Meat-type Quails (Coturnix coturnix coturnix) in the State of São Paulo, Brazil. Revta Bras. Ciênc. Avícola 15(3):169-286. pesquisou Salmonella spp. em codornas e observou 75% de positividade, e S. Lexington foi recuperada do tanque de escaldagem, água de refrigeração e carcaças.
O fato de diferentes sorovares terem sido isolados em um mesmo ponto de amostragem ou por métodos microbiológicos diversos, ou ainda sem relação entre swabs de cloaca e gaiolas de transporte (Quadro 2) seria mais um indicativo da complexidade do ciclo de infecção e reinfecção por Salmonella e da dificuldade em se estabelecer programas de controle efetivos para o patógeno, em consonância com Müller et al. (2009)Müller M., Schwarz P., Kich J.D.& Cardoso M. 2009. Perfil sorológico e de isolamento de Salmonella sp. em suínos no início da terminação e ao abate. Ciênc. Anim. Bras. 10(3):931-937., para quem a infecção por múltiplos sorovares é uma característica já reconhecida em suínos, mesmo em amostras colhidas de um mesmo animal.
A infecção por Salmonella pode ter origens distintas nas granjas comerciais e em abatedouros, o que justifica a variabilidade dos sorovares encontrados em cada região (Alban & Stark 2005Alban L. & Stärk K.D.C. 2005. Where should the effort be put to reduce the Salmonella presence in the slaughtered swine carcass effectively? Prev.Vet. Med., Amsterdam, 68:63-79.). No Brasil, destacam-se estudos sobre sorovares isolados na região sul (Castagna et al. 2001Castagna S.M.F., Bessa M.C., Carvalho D.A., Cardoso M.& Costa M. 2001. Resistência a antimicrobianos de amostras de Salmonella sp. isoladas de suínos abatidos no estado do rio grande do sul. Arqs Fac. Vet. UFRGS. 29(1):44-49., Bandeira et al. 2007Bandeira R., Pelegrini D.C.P. & Cardoso M. 2007. Ocorrência de Salmonella sp. em cortes de pernil provenientes de lotes suínos portadores ao abate. Acta Scientiae Veterinariae, Porto Alegre, 35:203-208., Spricigo et al. 2008Spricigo D.A., Matsumoto S.R., Espíndola M.L. & Ferraz S.M. 2008. Prevalência, quantificação e resistência a antimicrobianos de sorovares de Salmonella isolados de linguiça fresca suína. Ciência e Tecnologia de Alimentos 28:779-785., Michael et al. 2008Michael G.B., Cardoso M.& Schwarz S. 2008. Molecular analysis of multi resistant porcine Salmonella entérica subsp. Entérica serovar Bredeney isolates from Southern Brazil: identification of resistance genes, integrons and a group II. J. Antimicrobial Agents 32:120-129., Müller et al. 2009Müller M., Schwarz P., Kich J.D.& Cardoso M. 2009. Perfil sorológico e de isolamento de Salmonella sp. em suínos no início da terminação e ao abate. Ciênc. Anim. Bras. 10(3):931-937., Kich et al. 2011Kich J.D., Coldebella A., Morés N., Nogueira M.G., Cardoso M., Fratamico P.M., Call J.E., Fedorka-Cray P. & Luchansky J.B. 2011. Prevalence, distribution, and molecular characterization of Salmonella recovered from swine finishing herds and a slaughter facility in Santa Catarina, Brazil. Int. J. Food Microbiol. 151:307-313.) e centro-oeste (Silva et al. 2009Silva M.C., Faria G.S., De Paula D.A.J., Martins R.P., Caramori Junior J.G., Kichi J.D., Colodel E.D., Nakazato L. & Dutra V. 2009. Prevalência de Salmonella sp. em suínos abatidos no Estado de Mato Grosso. Ciência Rural 39:266-268.) onde são observadas diferenças entre os sorovares isolados em cada estudo, possivelmente devido a extensão do país e a variedade da produção animal.
Conclusões
Não foi possível correlacionar os resultados da microbiologia convencional e do mNMP ou mesmo quantificar a contaminação nos pontos amostrados, indicando a necessidade de aliar métodos qualitativos e quantitativos para identificação de Salmonella spp. em pontos críticos de controle no abate de frangos de corte.
Os sorovares identificados são considerados paratíficos e portanto potencialmente capazes de causar infecções em humanos.
A identificação de Salmonella spp. nas gaiolas de transporte após a higienização é um indicativo da necessidade de revisão e adequação dos métodos automatizados de lavagem atualmente utilizados nos abatedouros.
Agradecimentos
Ao apoio financeiro do CNPq, via Edital MCT/CNPq/MAPA/DAS nº 64/2008 - Ações de Defesa Agropecuária, sob o número 578124/2008-4.
- Alban L. & Stärk K.D.C. 2005. Where should the effort be put to reduce the Salmonella presence in the slaughtered swine carcass effectively? Prev.Vet. Med., Amsterdam, 68:63-79.
- Baggensen D.L., Bagger J., Mogelmose V., Nielsen B., Svensmark B. & Olsen J.E. 2001. Quantification of DT104 in slurry from infected pigs. Report on the 6th CRL-Salmonella Workshop, Bilthoven, Netherlands, p.30-32.
- Bandeira R., Pelegrini D.C.P. & Cardoso M. 2007. Ocorrência de Salmonella sp. em cortes de pernil provenientes de lotes suínos portadores ao abate. Acta Scientiae Veterinariae, Porto Alegre, 35:203-208.
- Bangtrakulnonth A., Pornreongwong S., Pulsrikarn C., Sawanpanyalert P., Hendriksen R.S., Wong D.M.A.L.F. & Aarestrup F.M. 2004. Salmonella serovars from humans and other sources in Thailand, 1993-2002. Emerg. Infect. Dis. 10:131-6.
- Benajssaum B.R., Gallasum N., Troudium B.H., Belhadjum B. & Belhadium A.B. 2007. Trends in Salmonella entérica serotypes isolated from food, humans, animals and environment in Tunisia, 1994-2004. J. Infection 55:324-339.
- Berchieri J., Freitas Neto O.C., Angela H.L., Soares N.M., Guastalli E.A.L. & Almeida A.M. 2013. Salmonella spp. in Meat-type Quails (Coturnix coturnix coturnix) in the State of São Paulo, Brazil. Revta Bras. Ciênc. Avícola 15(3):169-286.
- Bessa M.C. 2006. Caracterização fenotípica e genotípica de amostras de Salmonella entérica sorovar Typhimurium isoladas de suínos no Rio Grande do Sul. Tese de Doutorado em Ciências Veterinárias, Faculdade de Veterinária, Universidade Federal do Rio Grande do Sul, Porto Alegre. 144p.
- Borowsky L.M., Bessa M.C., Cardoso M.& Avancini C.A.M. 2006. Sensibilidade e resistência de amostras de Salmonella Typhimurium isoladas de suínos abatidos no Rio Grande do Sul/Brasil frente aos desinfetantes químicos quaternário de amônio e iodofor. Ciência Rural 36(5):1474-1479.
- Castagna S.M.F., Bessa M.C., Carvalho D.A., Cardoso M.& Costa M. 2001. Resistência a antimicrobianos de amostras de Salmonella sp. isoladas de suínos abatidos no estado do rio grande do sul. Arqs Fac. Vet. UFRGS. 29(1):44-49.
- Castelijn G.A.A., Parabirsing J.A., Zwietering M.H., Moezelaar R. & Abee T. 2013. Surface behavior of S. Typhimurium, S. Derby, S. Bradenburg and S. Infantis. Vet. Microbiol. 161: 305-314.
- Cavada C.A., Cardoso F.M. & Schimidt V. 2010. Comparison of three me-thods for Salmonella sp. quantification in wastwater. Acta Scientiae Veterinariae 38(1):17-23.
- Chen L., Zhang J., Yang X., Wu Q. & Xu M. 2013. [Prevalence and characterization of Salmonella spp. from foods in South China]. [Article in Chinese] .Wei Sheng Wu Xue Bao 453(12):1326-1333.
- Colla F.L., Mion L., Parizotto L., Rodrigues L.B., Pilotto F., Dickel E.L., Nascimento V.P. & Santos L.R. 2014. Miniaturized most probable number for the enumeration of Salmonella sp in artificially contaminated chicken meat. Revta Bras. Ciênc. Avícola 16(1):45-48.
- Corry J.E.L., Allen V.M. & Hudson W.R. 2002. Sources of Salmonella on broiler carcasses during transportation and processing: modes of contamination and methods of control. J. Appl. Microbiol. 92:424-432.
- Dickel E.L., Santos L.R., Rodrigues L.B., Valle S.F. & Cecatti D. 2005. Ocorrência de Salmonella em abatedouros de aves com tecnologia totalmente automatizada (grande porte), semi automatizada (médio porte) e semi automatizada (pequeno porte). Higiene Alimentar, São Paulo, 19(131):62-67.
- Duarte D.A.M., Ribeiro A.R., Vasconcelos A.M.M., Santos S.B., Silva J.V.D., Andrade P.L.A. & Falcão L. 2009. Occurrence of Samonella spp. in broiler chicken carcasses and their susceptibility to antimicrobial agents. Braz. J. Microbiol. 40(3):569-573.
- Fernandes S.A., Tavechio A.T., Ghilardi A.C.R., Dias A.M.G., Almeida I.A. & Melo L.C.V. 2006. Salmonella serovars isolated from humans in São Paulo State, Brazil, 1996-2003. Revta Inst. Med. Trop. São Paulo 48: 174-189.
- Fravalo P., Hascoet Y., Le Fellic M., Quegumer S., Petton J. & Salvat G. 2003. Convenient method for rapid and quantitative assessment of Salmonella enteric contamination: the mini-MSRV MPN technique. J. Rapid Methods and Automation in Microbiology 11(2):81- 88.
- Gast R., Guraya R. & Guard-Bouldin J. 2007. Colonization of specific regions of the reproductive tract and deposition at different locations inside eggs laid by hens infected with Salmonella Enteritidis or Salmonella Heidelberg. Avian Dis. 51:40-44.
- Gomes-Neves E., Antunes P., Tavares A., Themudo P., Cardoso M.F., Gärtner F., Costa J.M. & Peixe L. 2012. Salmonella cross contamination in swine abattoirs in Portugal: Carcasses, meat and meathandlers. Int. J. Food Microbiol. 157:82-87.
- Hofer E., Silva S.J. & Reis E.M.F. 2007. Prevalência de sorovares de Salmonella isolados de aves no Brasil. Pesq. Vet. Bras. 18(1):21-27.
- Humphrey T. & Jorgensen F. 2006. Pathogens on meat and infection in animals. Establishing a relationship using Campylobacter and Salmonella as examples. Meat Science 74:89-97.
- Kich J.D., Coldebella A., Morés N., Nogueira M.G., Cardoso M., Fratamico P.M., Call J.E., Fedorka-Cray P. & Luchansky J.B. 2011. Prevalence, distribution, and molecular characterization of Salmonella recovered from swine finishing herds and a slaughter facility in Santa Catarina, Brazil. Int. J. Food Microbiol. 151:307-313.
- Kumar S., Sadana J.R. & Mishra S.K. 2001. Studies on clinical signs, growth response and haematological changes in Japanese quail (Coturnix coturnix japonica) infected with Salmonella typhimurium. Indian J. Poult. Sci. 36:335-337.
- Lillard H.S. 1990. The Impact of commercial processing procedures on the bacterial contamination and cross-contamination of broiler carcasses. J. Food Protection 53(3):202-204.
- Mazengia E., Samadpour M., Hill H.W., Greeson K., Tenney K., Liao G., Huang X. & Meschke J.S. 2014. Prevalence, concentrations, and antibiotic sensitivities of Salmonella serovars in poultry from retail establishments in Seattle, Washington. J. Food Protection 77(6):885-93.
- Methner U., Rammler N., Fehlhaber K. & Rösler U. 2011. Salmonella status of pigs at slaughter - Bacteriological and serological analysis. Int. J. Food Microbiol. 151:15-20.
- Michael G.B., Cardoso M.& Schwarz S. 2008. Molecular analysis of multi resistant porcine Salmonella entérica subsp. Entérica serovar Bredeney isolates from Southern Brazil: identification of resistance genes, integrons and a group II. J. Antimicrobial Agents 32:120-129.
- Moreira G.N., Rezende C.S.M., Carvalho R.N., Mesquita S.Q.P., Oliveira A.N. & Arruda M.L.T. 2009. Ocorrência de Salmonella sp. em carcaças de frangos abatidos e comercializados em municípios do estado de Goiás. Revta Inst. Adolfo Lutz 67(2):126-130.
- Mueller-Doblies D., Speed K. & Davies R.H. 2013. A retrospective analysis of Salmonella serovars isolated from pigs in Great Britain between 1994 and 2010. Prev. Vet. Med. 110:447-455.
- Müller M., Schwarz P., Kich J.D.& Cardoso M. 2009. Perfil sorológico e de isolamento de Salmonella sp. em suínos no início da terminação e ao abate. Ciênc. Anim. Bras. 10(3):931-937.
- Noel H., Hofhuis A., De Jong R., Heuvelink A.E., De Jong R.& Jager C. 2010. Consumption of Fresh Fruit Juice: How a Healthy Food Practice Caused a National Outbreak of Salmonella Panama Gastroenteritis. Foodborne Pathogens and Disease 7(4):375-381.
- Patterson J.T. 1971. Microbiological aspects of poutry processing. Brit. Poult. Sci. 12:197-203.
- Phan T.T., Khai L.T., Ogasawara N., Tam N.T., Okatani A.T., Akiba M. & Hayashidani H. 2005. Contamination of Salmonella in retail meats and shrimps in the Mekong Delta, Vietnam J. Food Protection 68:1077-1080.
- Pavic A., Groves P.J., Bailey G. & Cox J.M. 2009. A validated miniaturized MPN method, based on ISO 6579:2002, for the enumeration of Salmonella from poultry matrices. J. Appl. Microbiol. 109:25-34.
- Ribeiro A.R., Kellermann A., Santos L.R. dos, Bessa M.C.& Nascimento V.P. do. 2007. Salmonella spp. in raw broiler parts: occurrance, antimicrobial resistance profile and phage typing of the Salmonella Enteritidis isolates. Braz. J. Microbiol. 38:296-299.
- Santos D.M.S., Berchieri Jr A., Fernandes S.A., Tavechio A.T.& Amaral L.A. 2000. Salmonella em carcaças de frango congeladas. Pesq. Vet. Bras. 20(1):39-42.
- Silva M.C., Faria G.S., De Paula D.A.J., Martins R.P., Caramori Junior J.G., Kichi J.D., Colodel E.D., Nakazato L. & Dutra V. 2009. Prevalência de Salmonella sp. em suínos abatidos no Estado de Mato Grosso. Ciência Rural 39:266-268.
- Simas V.S., Santos F.F., Gouvêa R., Aquino M.H.C., Abreu D.L.C., Nascimento E.R. & Pereira V.L.A. 2011.Pré-resfriamento na redução de coliformes em carcaças de frango de corte. Ciência Rural 43(9):1618-1622.
- Skovgaard N. 2005. Current topics in food microbiology. Int. J. Food Microbiol. 99:107-111.
- Skjerve E. & Olsvik O. 1991. Immunomagnetic separation of Salmonella from foods. Int. J. Food Microbiol. 14:11-18.
- Spricigo D.A., Matsumoto S.R., Espíndola M.L. & Ferraz S.M. 2008. Prevalência, quantificação e resistência a antimicrobianos de sorovares de Salmonella isolados de linguiça fresca suína. Ciência e Tecnologia de Alimentos 28:779-785.
- Ta Y.T., Nguyen T.T., To P.B., Pham X., Le H.T., Thi G.N., Alali W.Q., Walls I. & Doyle M.P. 2014. Quantification, serovars, and antibiotic resistance of Salmonella isolated from retail raw chicken meat in Vietnam. J. Food Protection77(1):57-66.
- Thomas H.A. 1942. Bacterial densities from fermentation tube tests. J. Am. Water Assoc. 34:572-576.
- USDA-FSIS 2008. Compliance Guideline for Controlling Salmonella and Campylobacter in Poultry. 2nd ed. Food Safety Inspection Service, United States Department of Agriculture, Washington, DC. Available at <http://www.fsis.usda.gov> Accessed in March 2013.
» http://www.fsis.usda.gov - Wang Y., Chen Q., Cui S., Xu X., Jianghui Zhu., Luo H., Wang D. & Li F. 2014. Enumeration and Characterization of Salmonella Isolates from Retail Chicken Carcasses in Beijing, China. Foodborne Pathogens and Disease 11(2):126-132.
- Yang B., Cui Y., Shi C., Wang J., Xia X., Xi M., Wang X., Meng J., Alali W.Q., Walls I.& Doyle M.P. 2014. Counts, serotypes, and antimicrobial resistance of Salmonella isolates on retail raw poultry in the People's Republic of China. J. Food Protection 77(6):894-902.
- Yang B., Qiao L., Zhang X., Cui Y., Xia X., Cui S., Wang X., Meng X., Ge W., Shi X., Wang D.& Meng J. 2013. Serotyping, antimicrobial susceptibility, pulse field gel electrophoresis analysis of Salmonella isolates from retail foods in Henan Province, China. Food Control, Guildford, 32:228-235.
Datas de Publicação
-
Publicação nesta coleção
Mar 2015
Histórico
-
Recebido
28 Jul 2014 -
Aceito
30 Dez 2014



 Thumbnail
Thumbnail