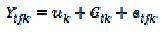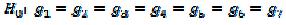RESUMO
Objetivou-se com este trabalho verificar a divergência genética entre sete genótipos de frangos tipo caipira da linhagem Redbro utilizando as características de desempenho por meio de técnicas de análise multivariada. Foram utilizados 840 pintos de um dia, machos, distribuídos em delineamento inteiramente ao acaso, dos seguintes genótipos: Caboclo, Carijó, Colorpak, Gigante Negro, Pesadão Vermelho, Pescoço Pelado e Tricolor. Após a consistência dos dados, foram avaliadas as seguintes variáveis: ganho em peso médio diário, consumo de ração médio diário e conversão alimentar, para os períodos: 1 a 28, 1 a 56, 1 a 70 e 1 a 84 dias de idade; peso corporal ao nascimento, aos 28, 56, 70 e aos 84 dias de idade. O desempenho dos genótipos foi avaliado por meio da análise de variância multivariada e da função discriminante linear de Fisher, usando os testes do maior autovalor de Roy e da união-interseção de Roy para as comparações múltiplas. O estudo da divergência genética foi feito por meio da análise por variáveis canônicas e pelo método de otimização de Tocher. Os genótipos Caboclo e Gigante Negro apresentaram médias canônicas diferentes dos demais genótipos. As duas primeiras variáveis canônicas explicaram 97,41% da variação entre os genótipos. A divergência genética entre os genótipos avaliados permitiu a formação de quatro grupos com os seguintes genótipos: grupo 1 - Colorpak; grupo 2 - Pesadão Vermelho e Pescoço Pelado; grupo 3 - Carijó e Tricolor; e grupo 4 - Caboclo e Gigante Negro.
agrupamento; análise discriminante; distância; variável canônica
ABSTRACT
The aim of this study was to evaluate the genetic divergence among seven genotypes of alternative strain of broiler chickens of the Redbro strain using the performance characteristics using multivariate analysis. We used 840 day old male chicks, distributed in a completely randomized design, with the following genotypes: Caboclo, Carijó, Colorpak, Gigante Negro, Pesadão Vermelho, Pescoço Pelado and Tricolor. After the consistency of the data, the following variables were analyzed: average daily gain, average daily feed intake and feed conversion for the periods: 1 to 28, 1 to 56, 1 to 70 and 1 to 84 days of age, body weight at birth, at 28, 56, 70 and at 84 days old. The performance of genotypes was assessed by multivariate analysis of variance and Fisher's linear discriminant function, using the tests of the largest eigenvalue of Roy and the Roy union-intersection for multiple comparisons. The study of genetic diversity was done by canonical variate analysis and the method of Tocher. The genotypes Caboclo and Gigante Negro had different canonical averages from the other genotypes. The first two canonical variables accounted for 97.41% of the variation among genotypes. The genetic divergence between the genotypes allowed the formation of four groups with the following genotypes: group 1 - Colorpak, group 2 - Pesadão Vermelho and Pescoço Pelado; group 3 - Carijó and Tricolor, and group 4 - Caboclo and Gigante Negro.
canonical variable; discriminant analysis; distance; group
INTRODUÇÃO
O melhoramento animal altera a composição gênica dos indivíduos, com intuito de atender à demanda dos produtores e consumidores, e, no melhoramento de aves, o principal objetivo é a melhoria no desempenho e no rendimento de carcaça das aves.
Considerando-se que as características de importância econômica, utilizadas para avaliar os indivíduos ou genótipos, são de natureza quantitativa e, portanto, sujeitas a diferentes bases genéticas e graus de influência de ambiente, torna-se difícil interpretar o conjunto de características a partir de análises univariadas (Sakaguti et al., 1996ROSTAGNO, H.S., ALBINO, L.F.T., DONZELE, J.L. et al. Composição de alimentos e exigências nutricionais: tabelas brasileiras. Viçosa, MG: Universidade Federal de Viçosa, 2005. 141p.). Para estudos em que várias variáveis devam ser consideradas simultaneamente, as técnicas de análise multivariada são métodos estatísticos mais apropriados (Franci et al., 2001FRANCI, O.; PULGLIESE, C.; BOZZI, R. et al. The use of multivariate analysis for evaluating relationships among fat depots in heavy pigs of different genotypes. Meat Sci., v.58, p.259-266, 2001.), pois combinam, simultaneamente, múltiplas informações provenientes de uma unidade experimental, que não são possíveis de serem obtidas com o uso da análise univariada (Viana et al., 2000SAKAGUTI, E.S.; SILVA, M.A.; REGAZZI, A.J. et al. Avaliação dos testes da análise de variância multivariada em experimentos com dados desbalanceados. Rev. Bras. Zootec., v.25, p.437-448, 1996.).
Uma técnica utilizada nos estudos de divergência genética é a análise por meio de variáveis canônicas, que consiste na transformação das variáveis originais em variáveis padronizadas e não correlacionadas, com a característica de manter o princípio do processo de conglomeração com base na distância D2 de Mahalanobis, descrita por Cruz e Regazzi (1997)CRUZ, C.D.; REGAZZI A.J. Modelos biométricos aplicados ao melhoramento genético. 2.ed. Viçosa, MG: UFV, 1997. 390p., além de considerar as matrizes de covariâncias residuais e fenotípicas das características avaliadas. O novo conjunto de varáveis, em ordem de estimação, retém o máximo de informação em termos de variação total. Essas variáveis explicarão tanto melhor a variabilidade manifestada entre os indivíduos avaliados quanto menor for o número de variáveis que acumulem pelo menos 80% da variação total (Fonseca et al., 2000FONSECA, R.; PIRES, A.V.; LOPES, P.S. et al. Estudo da divergência genética entre raças suínas utilizando técnicas de análise multivariada. Arq. Bras. Med. Vet. Zootec., v.52, p.403- 409, 2000.).
Ao determinar o número de variáveis canônicas que acumulam um mínimo de 80% da variância total disponível, estimam-se os escores de cada variável canônica que podem ser plotados em gráficos bi ou tridimensionais, sendo as variáveis canônicas usadas como eixos de referência, em que podem ser visualizadas as distâncias gráficas que representam as similaridades e dissimilaridades entre genótipos (Piassi et al., 1995PIASSI, M.; SILVA M.A.; REGAZZI, A.J. et al. Avaliação de diferentes grupos genéticos de aves de postura, usando-se análise de variância multivariada. Rev. Bras. Zootec., v.24, p.453-460, 1995a.b).
Com isso, objetivou-se com este trabalho verificar a divergência genética entre sete genótipos de frangos tipo caipira utilizando as características de desempenho por meio de técnicas de análise multivariada.
MATERIAL E MÉTODOS
O experimento foi conduzido no Setor de Avicultura do Departamento de Zootecnia da Universidade Federal dos Vales do Jequitinhonha e Mucuri, situado no Campus JK, em Diamantina-MG, durante o período de 21 de fevereiro a 16 de maio de 2011, sendo conduzido e aprovado de acordo com as normas do Comitê de Ética e Biossegurança da UFVJM, nº 015/10.
Foram utilizados 840 pintos de um dia, machos, provenientes de sete genótipos de frangos tipo caipira da linhagem Redbro: Caboclo (CBC), Carijó (CG), Colorpak (CPK), Gigante Negro (GNG), Pesadão Vermelho (PS), Pescoço Pelado (PP) e Tricolor (TRC), distribuídos em um delineamento inteiramente ao acaso, com quatro repetições (boxes) para cada genótipo. Os animais foram alojados em 28 boxes de dimensões 2,00 x 1,50m em galpão de alvenaria, coberto com telhas de fibrocimento, em quatro repetições (boxes) para cada genótipo, sendo 30 aves por boxe. A partir dos 28 dias de idade, as aves tiveram acesso a um piquete de 45m², formado por forrageira do tipo Tifton, gênero Cynodon.
As rações utilizadas foram formuladas à base de milho e farelo de soja, para as fases inicial (1 a 28 dias), crescimento (28 a 56 dias) e final (56 a 84 dias), conforme apresentado na Tabela 1, segundo informações de composições e digestibilidade dos ingredientes apresentadas em Rostagno et al. (2005)REGAZZI, A. J. Análise multivariada: notas de aula. Viçosa: UFV, 2002.; Mendonça et al. (2008); Nagib Nascimento et al. (2009)NAGIB NASCIMENTO, D.C.; SAKOMURA, N.K.; SIQUEIRA, J.C. et al. Exigências de lisina digestível para aves de corte da linhagem ISA Label criadas em semiconfinamento. Arq. Bras. Med. Vet. Zootec., v.61, p.1128-1138, 2009. ; Pinheiro et al. (2011)PINHEIRO, S.R.F.; SAKOMURA, N.K.; NAGIB NASCIMENTO, D.C. et al. Níveis nutricionais de fósforo disponível para aves de corte ISA Label criadas em semiconfinamento. Rev. Bras. Zootec., v.40, p.361-369, 2011..
As rações foram fornecidas à vontade, 24 horas por dia, até os 70 dias de idade. Após esse período, os animais passaram por restrição alimentar quantitativa, e receberam ração à vontade apenas das 9 às 16 horas.
As características de desempenho avaliadas foram: ganho em peso médio diário (GPMD), consumo de ração médio diário (CRMD) e conversão alimentar (CA), para os períodos: 1 a 28 dias (GPMD1-28, CRMD1-28 e CA1-28, respectivamente), 1 a 56 dias (GPMD1-56, CRMD1-56 e CA1-56, respectivamente), 1 a 70 dias (GPMD1-70, CRMD1-70 e CA1-70, respectivamente) e 1 a 84 dias (GPMD1-84, CRMD1-84 e CA1-84, respectivamente); além do peso corporal ao nascimento (PNASC), aos 28 (P28), 56 (P56), 70 (P70) e aos 84 dias de idade (P84).
As análises estatísticas foram feitas utilizando-se o procedimento "proc candisc" do programa SAS (2002), segundo o modelo:
em que:
 = valor observado da característica k, na repetição j, do genótipo i (i= 1, 2, ..., 7; j = 1, 2, 3, 4; k = 1, 2, ..., 17);
= valor observado da característica k, na repetição j, do genótipo i (i= 1, 2, ..., 7; j = 1, 2, 3, 4; k = 1, 2, ..., 17);
 média da característica k;
média da característica k;
 efeito do genótipo i na característica k;
efeito do genótipo i na característica k;
 = erro aleatório associado à observação
= erro aleatório associado à observação  .
.
Foi adotado o critério de descarte das variáveis, de acordo com a avaliação da importância das características, a partir dos coeficientes de ponderação de cada característica nas últimas variáveis canônicas que, por estimação, retêm proporção mínima da variação total (Regazzi, 2002).
Após o descarte dessas variáveis, foram feitos os testes de médias para a comparação entre os genótipos com as características que foram mantidas.
Em contraste com a análise univariada, na MANOVA obtêm-se matrizes A, H e E de soma de quadrados e produtos, com dimensões treze por treze (número de características avaliadas); sendo A, H e E as matrizes de soma de quadrados e produtos totais, de genótipos (tratamentos) e residuais, respectivamente. A hipótese testada pela MANOVA é a de igualdade dos vetores de médias entre os genótipos, ou seja:
Para testar essa hipótese, foi utilizado o teste do maior autovalor de Roy, que consiste na determinação das raízes características (autovalores) da equação característica
em que:
 matriz identidade;
matriz identidade;
 autovalores;
autovalores;
 inversa da matriz de soma de quadrados e produtos residual; e
inversa da matriz de soma de quadrados e produtos residual; e  matriz de soma de quadrados e produtos de tratamentos.
matriz de soma de quadrados e produtos de tratamentos.
Sendo λmax o maior autovalor de  , define-se a estatística
, define-se a estatística  .
.
O valor assim obtido Morrison, 1967MORRISON, D.F. Multivariate statistical methods. New York: McGraw- Hill, 1967. 338p.; Harris, 1975HARRIS, R.J. A primer of multivariate statistics. New York: Academic, 332p.).  é comparado com o limite de significância fornecido em tabelas (
é comparado com o limite de significância fornecido em tabelas (
A seguir realizou-se o teste de comparações de contrastes entre médias, pelo teste da união-interseção de Roy. Para a análise de agrupamento, foi utilizado o método de otimização de Tocher, adotando-se a distância D2 de Mahalanobis como medida de dispersão, conforme citado por Rao (1952)PIRES, A.V.; FONSECA, R.; COBUCI, J.A. et al. Estudo da divergência genética entre as raças suínas Duroc, Landrace e Large White, utilizando técnicas de análise multivariada. Arch. Lat. Prod. Anim., v.10, p.81-85, 2002.. Vários autores utilizaram esses testes para o estudo de divergência genética (Piassi et al., 1995a; Piassi et al., 1995b; Fonseca et al., 2000; Viana et al., 2000).
A função discriminante linear de Fisher (FDF) foi utilizada para testar a diferença entre os genótipos (tratamentos). Os coeficientes da FDF, já aplicada aos dados de observações, reduzem o espaço kdimensional a um espaço unidimensional, conservando a informação da variabilidade contida nos dados. A partir desse ponto, realizou-se uma ANOVA em que a hipótese testada foi de igualdade dos genótipos (tratamentos):
Para testar contrastes entre as médias dos genótipos (tratamentos), foi calculada a diferença mínima significativa (DMS):
em que:
 valor crítico de Roy, a 1% de probabilidade;
valor crítico de Roy, a 1% de probabilidade;
i;  número de repetições para o genótipo
número de repetições para o genótipo
 soma de quadrados do resíduo.
soma de quadrados do resíduo.
RESULTADOS E DISCUSSÃO
Verificou-se que as variáveis GPMD1-28, P84, GPMD1-84 e P56 são passíveis de descarte, pois retêm proporção mínima da variação total, por apresentarem maiores valores absolutos nas últimas variáveis canônicas (Can6, Can5, Can4 e Can3, respectivamente), como pode ser visualizado na Tabela 2, e representam, portanto, uma variação praticamente insignificante (Regazzi, 2002).
A partir do coeficiente canônico 2 (Can2), não se eliminou nenhuma variável, uma vez que a característica GPMD1-84 já havia sido eliminada anteriormente.
A partir das análises, considerando apenas as características não descartadas, foi observada diferença significativa (P≤0,01) entre os genótipos pelo teste de Roy, conforme pode ser visto na Tabela 3, para as características GPMD1-56, GPMD1-70 e P70, podendo ser notado que os genótipos Caboclo e Gigante Negro apresentaram o pior desempenho, já o Colorpak obteve o melhor desempenho nas respectivas características.
Há diferença (P≤0,01) no desempenho entre os genótipos avaliados pelo teste de Roy, aplicado à função discriminante de Fischer - FDF, conforme pode ser visto na Tabela 4. O genótipo Colorpak apresentou maior média, não diferindo estatisticamente do Pesadão Vermelho, Pescoço Pelado e Carijó; já os genótipos Caboclo e Gigante Negro apresentaram as menores médias. O desempenho de cada genótipo para cada característica estudada é explicado pelo teste do maior autovalor de Roy. Neste trabalho, as informações obtidas foram empregadas para comparação entre genótipos, mas também são aplicadas na avaliação entre linhagens de uma mesma raça nos rebanhos núcleos, como nos estudos de Viana et al. (2000) e Carneiro et al. (2002)CARNEIRO, P.L.S.; FONSECA, R; PIRES, A.V. et al. Estudo da divergência genética entre linhagens de matrizes de frangos de corte por meio de análise multivariada. Arq. Bras. Med. Vet. Zootec., v.54, p.75-83, 2002., quando as informações alcançadas foram aproveitadas em conjunto com outras informações para descarte e/ou seleção de linhagens. Pela FDF ou primeira variável canônica, consegue-se ter uma visão aproximada do comportamento geral do genótipo, considerando-se todas as características agrupadas em um único índice, o escore da FDF.
A técnica de variáveis canônicas é, geralmente, considerada eficiente quando a maior parte da variação entre as características pode ser explicada nos três primeiros componentes principais, uma vez que a transformação na nova escala conserva toda a variabilidade explicada pelas variáveis na escala original, resultando em variáveis não correlacionadas.
As duas primeiras variáveis canônicas explicaram 97,41% da variação observada, conforme apresentado na Tabela 5 e, portanto, foram utilizadas para gerar as duas médias canônicas utilizadas na representação bidimensional, podendo ser visualizada na Figura 1, a partir da qual se podem visualizar as distâncias gráficas que representam as similaridades e dissimilaridades entre os genótipos.
Variáveis canônicas, autovalores e percentagens da variância obtidas da análise das características para os sete genótipos de frangos tipo caipira
A partir das duas primeiras médias canônicas, MC1 e MC2, apresentadas na Tab. 6, utilizadas para a dispersão gráfica (Fig. 1), verificaram-se grandes diferenças numéricas entre as mesmas e que essas diferenças são maiores na MC1 e menores na MC2, devido ao fato de a VC1, diretamente relacionada à MC1, reter a maior proporção da variação dos dados, 87,82% (Tab. 5). As diferenças são tão grandes que os genótipos Caboclo e Gigante Negro apresentaram a MC1 com valor negativo, e, portanto, média em sentido oposto à dos outros genótipos, o que evidencia que esses genótipos são muito diferentes geneticamente dos demais e próximos do frango caipira, que pode ser comprovado pelo seu desempenho muito inferior aos demais.
Com relação à segunda média canônica (MC2), os resultados já foram menos discrepantes, fato este justificado pelo percentual da variância total explicado pela VC2 (Tab. 5).
Os sete genótipos também foram agrupados pelo método de otimização de Tocher, resultando na formação de quatro grupamentos genéticos, representados pelos círculos na Figura 1, que representam a similaridade genética dentro do grupo e a divergência genética entre os grupos. Os genótipos Pesadão Vermelho e Pescoço Pelado foram agrupados num mesmo conjunto, o mesmo pôde ser observado para o Carijó e Tricolor; Caboclo e Gigante Negro; e o genótipo Colorpak formou um grupo sem mais nenhum outro genótipo, evidenciando a distância genética das aves Colorpak em relação aos demais genótipos avaliados. O fato de os genótipos Caboclo e Gigante Negro terem ficado sozinhos em um único grupo pode ser explicado pelo fato de serem aves de crescimento lento e mais leves, estando mais próximos geneticamente do frango caipira, e, em contrapartida, o Colorpak, que formou um único grupo, estar mais próximo do frango de corte convencional.
Outros estudos de agrupamento entre genótipos foram realizados por Pires et al. (2002)PINHEIRO, S.R.F.; SAKOMURA, N.K.; SIQUEIRA, J.C. et al. Níveis nutricionais de cálcio para aves de corte ISA Label criadas sob semiconfinamento. Arq. Bras. Med. Vet. Zootec., v.63, p.231-238, 2011. com suínos, Yamaki et al. (2008)VIANA, C.F.A.; SILVA M.A.; PIRES A.V. et al. Estudo da divergência genética entre quatro linhagens de matrizes de frangos de corte utilizando técnicas de análise multivariada. Rev. Bras. Zootec., v.29, p.1074-1081, 2000. com matrizes de frangos de corte e Machado et al. (2010)MACHADO, T.M.M.; PIRES, L.C; ARAUJO, A.M. et al. Diversidade biométrica entre populações caprinas no Brasil e no Marrocos. In: REUNIÃO ANUAL DA SOCIEDADE BRASILEIRA DE ZOOTECNIA, 47., 2010, Salvador. Anais... Salvador: SBZ, 2010. (CD-ROM). .
CONCLUSÕES
De maneira geral, as aves do genótipo Colorpak apresentaram melhor desempenho, enquanto as Caboclo e Gigante Negro obtiveram os piores desempenhos. A divergência genética entre os genótipos avaliados permitiu a formação de quatro grupos com os seguintes genótipos: grupo 1 - Colorpak; grupo 2 - Pesadão Vermelho e Pescoço Pelado; grupo 3 - Carijó e Tricolor; e grupo 4 - Caboclo e Gigante Negro.
AGRADECIMENTOS
Os autores agradecem o aporte financeiro e apoio recebidos da Avifran, CAPES, CNPq, Fapemig e Globoaves.
REFERÊNCIAS
- CARNEIRO, P.L.S.; FONSECA, R; PIRES, A.V. et al. Estudo da divergência genética entre linhagens de matrizes de frangos de corte por meio de análise multivariada. Arq. Bras. Med. Vet. Zootec., v.54, p.75-83, 2002.
- CRUZ, C.D.; REGAZZI A.J. Modelos biométricos aplicados ao melhoramento genético. 2.ed. Viçosa, MG: UFV, 1997. 390p.
- FONSECA, R.; PIRES, A.V.; LOPES, P.S. et al. Estudo da divergência genética entre raças suínas utilizando técnicas de análise multivariada. Arq. Bras. Med. Vet. Zootec., v.52, p.403- 409, 2000.
- FRANCI, O.; PULGLIESE, C.; BOZZI, R. et al. The use of multivariate analysis for evaluating relationships among fat depots in heavy pigs of different genotypes. Meat Sci., v.58, p.259-266, 2001.
- HARRIS, R.J. A primer of multivariate statistics. New York: Academic, 332p.
- MACHADO, T.M.M.; PIRES, L.C; ARAUJO, A.M. et al. Diversidade biométrica entre populações caprinas no Brasil e no Marrocos. In: REUNIÃO ANUAL DA SOCIEDADE BRASILEIRA DE ZOOTECNIA, 47., 2010, Salvador. Anais... Salvador: SBZ, 2010. (CD-ROM).
- MENDONÇA, M.O.; SAKOMURA, N.K.; SANTOS, F.R. et al. Níveis de energia metabolizável para machos de corte de crescimento lento criados em semiconfinamento. Rev. Bras. Zootec., v.37, p.1433-1440, 2008.
- MORRISON, D.F. Multivariate statistical methods. New York: McGraw- Hill, 1967. 338p.
- NAGIB NASCIMENTO, D.C.; SAKOMURA, N.K.; SIQUEIRA, J.C. et al. Exigências de lisina digestível para aves de corte da linhagem ISA Label criadas em semiconfinamento. Arq. Bras. Med. Vet. Zootec., v.61, p.1128-1138, 2009.
- NAGIB NASCIMENTO, D.C.; SAKOMURA, N.K.; SIQUEIRA, J.C. et al. Exigências de metionina + cistina digestível para aves de corte ISA Label criadas em semiconfinamento. Rev. Bras. Zootec., v.38, p.869-878, 2009.
- PIASSI, M.; SILVA M.A.; REGAZZI, A.J. et al. Avaliação de diferentes grupos genéticos de aves de postura, usando-se análise de variância multivariada. Rev. Bras. Zootec., v.24, p.453-460, 1995a.
- PIASSI, M.; SILVA, M.A.; REGAZZI, R.J. et al. Estudo da divergência genética entre oito grupos de aves de postura por meio de técnicas de análise multivariada. Rev. Bras. Zootec., v.24, p.715-727, 1995b.
- PINHEIRO, S.R.F.; SAKOMURA, N.K.; NAGIB NASCIMENTO, D.C. et al. Níveis nutricionais de fósforo disponível para aves de corte ISA Label criadas em semiconfinamento. Rev. Bras. Zootec., v.40, p.361-369, 2011.
- PINHEIRO, S.R.F.; SAKOMURA, N.K.; SIQUEIRA, J.C. et al. Níveis nutricionais de cálcio para aves de corte ISA Label criadas sob semiconfinamento. Arq. Bras. Med. Vet. Zootec., v.63, p.231-238, 2011.
- PIRES, A.V.; FONSECA, R.; COBUCI, J.A. et al. Estudo da divergência genética entre as raças suínas Duroc, Landrace e Large White, utilizando técnicas de análise multivariada. Arch. Lat. Prod. Anim., v.10, p.81-85, 2002.
- RAO, C.R. Advanced statistical methods in biometric research. New York: Jonh Wiley & Sons, 1952. 390p.
- REGAZZI, A. J. Análise multivariada: notas de aula. Viçosa: UFV, 2002.
- ROSTAGNO, H.S., ALBINO, L.F.T., DONZELE, J.L. et al. Composição de alimentos e exigências nutricionais: tabelas brasileiras. Viçosa, MG: Universidade Federal de Viçosa, 2005. 141p.
- SAKAGUTI, E.S.; SILVA, M.A.; REGAZZI, A.J. et al. Avaliação dos testes da análise de variância multivariada em experimentos com dados desbalanceados. Rev. Bras. Zootec., v.25, p.437-448, 1996.
- VIANA, C.F.A.; SILVA M.A.; PIRES A.V. et al. Estudo da divergência genética entre quatro linhagens de matrizes de frangos de corte utilizando técnicas de análise multivariada. Rev. Bras. Zootec., v.29, p.1074-1081, 2000.
- YAMAKI, M.; MENEZES, G.R.O.; TEIXEIRA, R.B. et al. Divergência genética entre linhagens de matrizes de corte por meio de análise de agrupamento. Rev. Bras. Zootec., v.37, p.829-833, 2008.
Datas de Publicação
-
Publicação nesta coleção
Out 2015
Histórico
-
Recebido
10 Fev 2014 -
Aceito
12 Mar 2015